Lượt truy cập 4.355.727
TIN TỨC

ĐẠI HỘI CHI ĐOÀN HỌC VIỆN KHOA HỌC VÀ CÔNG NGHỆ NHIỆM KỲ 2024 -2027 
Hòa chung không khí thi đua sôi nổi chào mừng kỉ niệm 93 năm ngày thành lập Đoàn TNCS Hồ Chí Minh (26/3/1931-26/3/2024) và hưởng ứng tháng thanh niên năm 2024, chiều ngày 25 tháng 03 năm 2024, Chi đoàn Học viện Khoa học và Công nghệ long trọng tổ chức Đại hội Chi đoàn nhiệm kỳ 2024 -2027.
-
 Lễ công bố Học bổng và hỗ trợ nghiên cứu khoa học do Tập đoàn NOVATECH tài trợ
Lễ công bố Học bổng và hỗ trợ nghiên cứu khoa học do Tập đoàn NOVATECH tài trợ
-
 Học viện Khoa học và Công nghệ tổ chức Lễ công bố và trao Quyết định bổ nhiệm chức danh Giáo sư, Phó Giáo sư năm 2023 và Lễ trao bằng Tiến sĩ đợt 2 năm 2023
Học viện Khoa học và Công nghệ tổ chức Lễ công bố và trao Quyết định bổ nhiệm chức danh Giáo sư, Phó Giáo sư năm 2023 và Lễ trao bằng Tiến sĩ đợt 2 năm 2023
-
 26 học viên cao học và nghiên cứu sinh xuất sắc của Học viện Khoa học và Công nghệ - Viện Hàn lâm Khoa học và Công nghệ Việt Nam nhận học bổng Vallet năm 2023
26 học viên cao học và nghiên cứu sinh xuất sắc của Học viện Khoa học và Công nghệ - Viện Hàn lâm Khoa học và Công nghệ Việt Nam nhận học bổng Vallet năm 2023
-
 Học viện Khoa học và Công nghệ tổ chức Lễ Trao bằng Thạc sĩ, Tiến sĩ đợt 1 năm 2023
Học viện Khoa học và Công nghệ tổ chức Lễ Trao bằng Thạc sĩ, Tiến sĩ đợt 1 năm 2023
THÔNG BÁO
- » THÔNG BÁO: Tuyển sinh đào tạo trình độ Thạc sĩ đợt 1 năm 2024
- » THÔNG BÁO: Tuyển sinh đào tạo trình độ Tiến sĩ đợt 1 năm 2024
- » THÔNG BÁO: Về việc xét duyệt học bổng do Tập đpàn Novatech tài trợ năm 2024
- » Học viện Khoa học và Công nghệ Thông báo: Về việc đăng ký đề tài và bảo vệ đề cương luận văn thạc sĩ đợt 1 năm 2024 (Khóa 2022B)
- » Học viện Khoa học và Công nghệ Thông báo: Về việc hồ sơ bảo vệ luận văn thạc sĩ đợt 1 năm 2024
TUYỂN SINH CAO HỌC
-
 Học viện Khoa học và Công nghệ Thông báo V/v phúc khảo bài thi môn Tiếng Anh tuyển sinh đào tạo trình độ thạc sĩ đợt 1 năm 2023.
Học viện Khoa học và Công nghệ Thông báo V/v phúc khảo bài thi môn Tiếng Anh tuyển sinh đào tạo trình độ thạc sĩ đợt 1 năm 2023.
-
 Kết quả tuyển sinh đào tạo trình độ thạc sĩ đợt 1 năm 2023.
Kết quả tuyển sinh đào tạo trình độ thạc sĩ đợt 1 năm 2023.
-
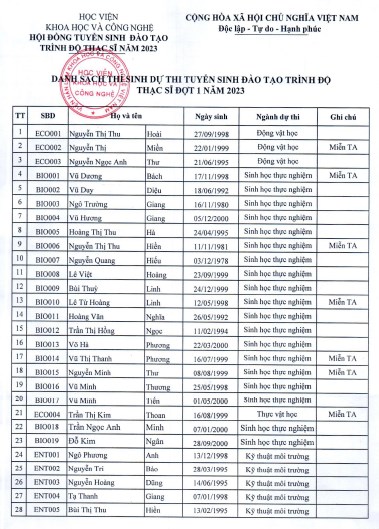 Học viện Khoa học và Công nghệ thông báo Danh sách thí sinh dự thi tuyển sinh đào tạo trình độ Thạc sĩ đợt 1 năm 2023
Học viện Khoa học và Công nghệ thông báo Danh sách thí sinh dự thi tuyển sinh đào tạo trình độ Thạc sĩ đợt 1 năm 2023
-
 Học viện Khoa học và Công nghệ thông báo Về việc kéo dài thời gian thu hồ sơ, hình thức thi và dạng thức đề thi môn Tiếng anh cho kỳ thi tuyển sinh đào tạo trình độ Thạc sĩ đợt 1 năm 2023
Học viện Khoa học và Công nghệ thông báo Về việc kéo dài thời gian thu hồ sơ, hình thức thi và dạng thức đề thi môn Tiếng anh cho kỳ thi tuyển sinh đào tạo trình độ Thạc sĩ đợt 1 năm 2023
TUYỂN SINH NGHIÊN CỨU SINH
-
 Học viện Khoa học và Công nghệ thông báo Về việc kéo dài thời gian thu hồ sơ tuyển sinh đào tạo trình độ Tiến sĩ đợt 1 năm 2023
Học viện Khoa học và Công nghệ thông báo Về việc kéo dài thời gian thu hồ sơ tuyển sinh đào tạo trình độ Tiến sĩ đợt 1 năm 2023
-
 Học viện Khoa học và Công nghệ Thông báo tuyển sinh đào tạo trình độ tiến sĩ đợt 1 năm 2023
Học viện Khoa học và Công nghệ Thông báo tuyển sinh đào tạo trình độ tiến sĩ đợt 1 năm 2023
-
 Học viện Khoa học và Công nghệ Thông báo tuyển sinh đào tạo trình độ Tiến sĩ đợt 2 năm 2022
Học viện Khoa học và Công nghệ Thông báo tuyển sinh đào tạo trình độ Tiến sĩ đợt 2 năm 2022
-
 Thông báo về việc kéo dài thời gian thu hồ sơ tuyển sinh đào tạo trình độ tiến sĩ đợt 1 năm 2022
Thông báo về việc kéo dài thời gian thu hồ sơ tuyển sinh đào tạo trình độ tiến sĩ đợt 1 năm 2022
 HỆ THỐNG PHÒNG THÍ NGHIỆM
HỆ THỐNG PHÒNG THÍ NGHIỆM
Hệ thống các phòng thí nghiệm trọng điểm Quốc gia của Viện Hàn lâm KH&CN Việt Nam cùng nhiều phòng thí nghiệm nghiên cứu của 35 viện nghiên cứu chuyên ngành

 CƠ SỞ DỮ LIỆU GIẢNG VIÊN
CƠ SỞ DỮ LIỆU GIẢNG VIÊN
Thông tin lý lịch khoa học, hướng nghiên cứu của giảng viên thuộc 12 khoa của Học viện Khoa học và Công nghệ

 CÔNG BỐ KHOA HỌC
CÔNG BỐ KHOA HỌC
Thông tin các công trình khoa học đã công bố của giảng viên, NCS thuộc 12 khoa của Học viện Khoa học và Công nghệ

 ĐỀ TÀI KHOA HỌC
ĐỀ TÀI KHOA HỌC
Thông tin về các đề tài nghiên cứu khoa học của Học viện Khoa học và Công nghệ đã và đang triển khai

 ĐỀ TÀI, NHIỆM VỤ SAU TIẾN SĨ (POSTDOC)
ĐỀ TÀI, NHIỆM VỤ SAU TIẾN SĨ (POSTDOC)
Thông tin về các đề tài, nhiệm vụ sau tiến sĩ của Học viện Khoa học và Công nghệ đang triển khai

 HỘI THẢO, HỘI NGHỊ
HỘI THẢO, HỘI NGHỊ
Thông tin chi tiết về các hội thảo, hội nghị khoa học hỗ trợ giảng viên, nghiên cứu sinh, học viên gửi bài tham dự


































